Ernst-Jan Eggers1,2, Ate van der Burgt1, Sjaak AW van Heusden2, Michiel E. de Vries@ 1, Richard GF Visser©2, Christian WB Bachem©2и & Pim Lindhout1
Patataren irabazi genetikoa landutako patataren genoma tetraploide heterozigotoak oztopatzen du. Patata F1-hibrido-linean oinarritutako endogamian oinarritutako laborantza diploide batean bihurtzeak bide itxaropentsua eskaintzen du irabazi genetikoa areagotzeko. Patata-geroplasma diploidean S-locus inhibitzaile (Sli) gene nagusi bat sartzeak autoernaldutako haziak modu eraginkorrean sortzea ahalbidetzen du, eta, beraz, patata endogamia-lerroak garatzea ahalbidetzen du. Gutxi dakigu Sli locusaren egituraz eta funtzioaz. Hemen Sli-ren mapaketa deskribatzen dugu 12.6. kromosomako 12 kb-ko tarte batean pantaila birkonbinatzaile baten ikuspegia erabiliz. Tarte honetan dauden bi gene hautagaietako batek lerro auto-bateragarrietan soilik dagoen sekuentzia berezia erakusten du. Auto-bateraezina bihurtzen duen adierazpen-bektore bat deskribatzen dugu genotipoak auto-bateragarria eta SC genotipoak SI bihurtzen dituen CRISPR-Cas9 bektore batean. Sli geneak F-box proteina bat kodetzen du, berariaz landare auto-bateragarrietako polenean adierazten dena. Gene horren sustatzailean 533 bp txertatzeak funtzio-mutazioaren irabazia dakar, eta horrek autopolenaren errefusa gainditzen du.
Patata munduko elikagairik gabeko labore garrantzitsuena da. Hala ere, beste elikagai-labore batzuek, hala nola artoa, arroza eta garia, urteko % 1eko etekin genetikoa izan duten bitartean.1, patataren irabazi genetikoa gutxienekoa izan da2. Gaur egun, komertzialki hazitako patata-labore gehienak guraso autotetraploide heterozigotoen arteko gurutzaketetatik eratorriak dira. Ugalketa-sistema honetan, ehunka mila landare sortzen eta aztertzen dira ugalketa-belaunaldi bakoitzean, ondorengoetan bereizten diren ezaugarri ugarientzako ezaugarri onargarriak dituzten banako arraro horiek identifikatzeko. Patata-hazkuntza komertzialen baliorako garrantzitsuak diren berrogeita hamar bat ezaugarri daudenez, ohiko patata-hazkuntza erabiliz ezaugarri horiek kontrolatzen dituzten alelo onenak konbinatzeko aukera arbuiagarria da. Horrez gain, eliteko kultiboetan ezaugarri berriak zuzenduta sartzea ezinezkoa da osotasun genetikoa mantenduz atzera-gurutzaketa eskemen bidez, guraso-lerro homozigotorik gabe. Arazo horiek gainditzeko, hainbat taldek endogamian oinarritutako patata diploideen hazkuntza programak hasi dituzte.2-5. Programa hauetan, irabazi genetikoak guraso-lerroen hobekuntzaren bidez lortzen dira, endogamian zehar alelo kaltegarrien aurka etengabe hautatuz eta endogamia-lerroetan alelo onuragarriak pilatuz atzera-gurutzaketa eskemen bidez.6. Ondoren, gurasoen endogamia-lerroak gurutzatzen dira F1-hibrido heterotikoen ondorengoak sortzeko.
Patata diploideen genotipo gehienetan, endogamia oso mugatuta dago auto-bateraezintasun gametofitiko (GSI) sistema batek, S-loku anitzeko alelikoak kontrolatzen duena. S-locus honek estiloan adierazitako S-RNasak kodetzen ditu, estiloan auto-polen-hodiaren hazkundea galarazten dutenak, auto-ernalketa saihestuz.7. Polinizazio gurutzatuan zehar, polenak adierazitako S-locus F-box proteinek (SLF) S-RNasak ezagutzen dituzte eta degradazio proteasomikoaren bidera bideratzen dituzte, ernalketa egin daitekeen obulutegietara hazten den polen-hodiak ahalbidetuz.8. S-alelo bakoitzak S-RNasa bat eta berezitasun ezberdineko SLF anitz kodetzen ditu, eta horiek elkarrekin S-RNasa guztiak ezagutu ditzakete alelo berean dagoen S-RNasa izan ezik.9.
Patata-lerro diploide gehienak berez bateraezinak (SI) badira ere, patata-lerro diploide auto-bateragarriak badira eta patata diploideen hazkuntza-programetan auto-bateragarritasuna sartzeko erabil daitezke.10-12. Hosakak eta Hannemanek S-locus inhibitzaile nagusi bat mapatu zuten (Sli) gene batetik Solanum chacoense 12. kromosomaren muturrean sartzea eta patata-lerro endogamiak sortzeko erabili zuen13'14. Euren emaitzetan oinarrituta, hori iradoki zuten Hosakak eta Hannemanek sli polen bidez adierazitako gene bat da, ekintza esporofitoa duena eta homozigositate hori sli hilgarria da homozigotoaz geroztik SliSli genotipoak ez zeuden S-ren F8 populazioan. chacoense. S hauetako bat erabili dugu. chacoense (DS) eratorritako lerro endogamiak S-en auto-bateragarritasuna sartzeko. tuberosum jatorriak. Hemen, autobateragarritasunaren kausazko genearen identifikazioa deskribatzen dugu patata diploidearen autobateragarritasunaren biologiari buruzko informazio gehiago lortzeko.
Emaitzak eta eztabaida
F2 populazio batean gurutzaketa batetik eratorritako sli emailea (DS izendatua) eta S diploide bat. tuberosum (D2) 2. kromosoman auto-baia ezarritako QTL efektu apala ikusi genuen, baina ondorengo baheketa birkonbinatzailea ez zen arrakastarik izan. F2 populazio anitzek 12. kromosomaren beso luzearen inguruan muturreko okertasuna erakusten zutela ohartu ginen, DS ez den haplotipoaren homozigositatea guztiz falta zela.
Okertze horretan eta ren mapak oinarri hartuta sli 12. kromosoman, hori planteatu genuen sli gametofitikoki adierazten da, hau da, landare baten autopolinizazioan heterozigotoa da sli (Sli/sli), dominantea duen polena bakarrik sli aleloak autoernalkuntzan parte har dezake. Hipotesi hau probatzeko, lerro indartsu eta oso auto-ernalgarri bat (16HP1-66) lerro indartsu bateraezin batera (D16) gurutzatu genuen, genoma osoak biak sekuentziatu genituen eta ondoriozko F1 populazioa aztertu genuen (17SC11, n = 251, irudia. 1a, b). F1 populazio hau loci askorentzat oso polimorfoa denez, fenotipo ugari ikusi ditugu, ugalkortasunarekin zerikusia dutenak barne. Hori dela eta, fenotipizazio-protokolo oso zorrotza eta zorrotza ezarri dugu, baia eta hazi multzoak bai gurutzatutako eta autopolinizazioetatik abiatuta, bai eta polen-hodiaren hazkuntza estiloetan bistaratzen dituena, esterilitate-arazoak bateragarritasun fenotipoa nahastea ekiditeko. Baia bat baino gehiago ezartzen duten landareak SC kontsideratzen dira, eta, aldiz, gutxienez 10 autopolinizazioren ondoren autopolinizazioaren ondoren auto-baia ezartzen ez duten landareak, auto-polen-hodiaren hazkuntza geldiarazten dute estiloan, eta bulked polinizazioaren ondoren gurutzatutako baiak ezartzen dituzte. polena SI kontsideratzen da. Ondorioz, populazioaren zati garrantzitsu bat analisi genetikoetatik kanpo geratu zen, bateragarritasun fenotipoa anbiguotasunik gabe ebaluatzeko baldintzak betetzen ez zirelako. Hala ere, biztanleriaren 17SC11 ondorengoen gehiengoaren bateragarritasun-egoera ebaluatu liteke eta auto-bateragarritasunerako bereizten zela frogatu zen (1. datu osagarriak). Auto-bateragarritasuna 16HP1-66tik sortu zenez, genotipo honen genoma sekuentzia osoak erabili genituen 2. eta 12. kromosometan SNPak diseinatzeko KASP markatzaileak diseinatzeko, 16HP1-66an heterozigotoak baina D16an homozigotoak, eta mapaketa ahalbidetuz. sli amaren meiosian. Mapa genetikoa egin genuen, QTL azterketa egin genuen eta QTL oso esanguratsua (LOD = 75.72) aurkitu genuen 12. kromosomaren beso luzean (Irudia. 1b), Hosaka eta Hannemanen emaitzak baieztatuz.
QTL beste jatorri genetiko batean baieztatzeko, Solynta ugalketa programatik eratorritako beste genotipo oso auto-ernal bat gurutzatu genuen SI D14 genotipoarekin eta ondoriozko F1 populazioa aztertu genuen (17SC25, Datu osagarriak 1). 32SC17 biztanleko 25 indibiduoren artean, ez dugu SI indibiduorik aurkitu. Populazio bereizgarria sortzeko, genotipo emankorrena hautatu genuen eta 17SC11 populazioan identifikatu genituen bi SI genotipoekin gurutzatu genuen, 18SC11 eta 18SC12 populazioak lortuz (1. datu osagarriak eta 1. irudi osagarria). Espero zen bezala, 18SC11 eta 18SC12 populazioen azterketak erakutsi zuen bi populazioak bereizten direla auto-bateragarritasunerako. Ama (17SC25-8) genoma osoa sekuentziatzeko bidali genuen eta datu hauek KASP markatzaile berriak diseinatzeko erabili genuen 17SC11 populazioan erabilitako ikuspegi bera erabiliz, baina oraingoan 12. kromosomari soilik zuzenduta. Ondorengo QTL analisiak populazioan aurkitu genuen QTL-a baieztatu zuen. 17SC11 33.14 eta 120.94 LOD balioekin 18SC11 eta 18SC12 populazioetan, hurrenez hurren (2. irudi osagarria).
Ea zehazteko sli gametofitikoki adierazten da, F2 populazio bat aztertu dugu (19SC1, n = 160) 17SC11 indibiduo emankor eta kementsu batetik eratorria. Populazio honen loraldia eta emankortasuna murriztu ziren F1arekin alderatuta. Azterketa fenotipikoan, 160 landareetatik, 81 landare auto-bateragarriak ziren, 78 zehaztu gabeko gisa sailkatu ziren (ND) loraldi eskasa edo ugalkortasun eskasa zela eta eta landare bat auto-bateragarritzat jo zuten (1. datu osagarriak). 12HP16-1 eta D66 gurasoen ordezko aleloetarako homozigotoak diren 16. kromosomako SNPak zuzendutako KASP markatzaileak diseinatu genituen. 12 kromosomaren bereizketa-ratioak nabarmen desbideratzen dira espero den 1:2:1 bereizketatik. Gainera, QTL autobateragarritasunaren inguruan, ez dago D16 gurasoaren haplotiporako loci homozigotorik (3. irudi osagarria), D1 / 1HP16-16 heterozigotoentzako 1:66 bereizketa erakusten duena: 16HP1-66 homozigotoa, eta horrek ezabatzea iradokitzen du. polena falta sli segregazioaren distortsioa eragiten du. Honek menperatzailea polena bakarrik daramala hipotesia onartzen du sli aleloak autoernalkuntzan parte hartzen du. Horrez gain, banako batez gain, fenotipatzea erabakigarria izan zen SI eta SC arteko kontrasterako, eta erabilitako fenotipizazio protokoloa sendoa eta ia akatsik gabekoa dela erakutsiz.
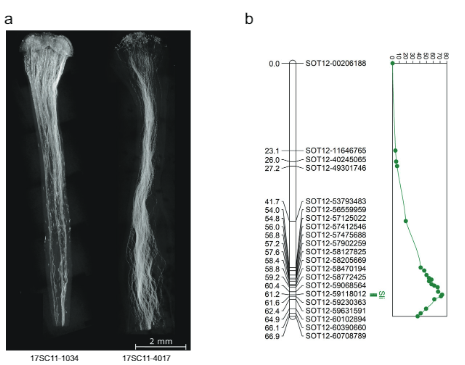
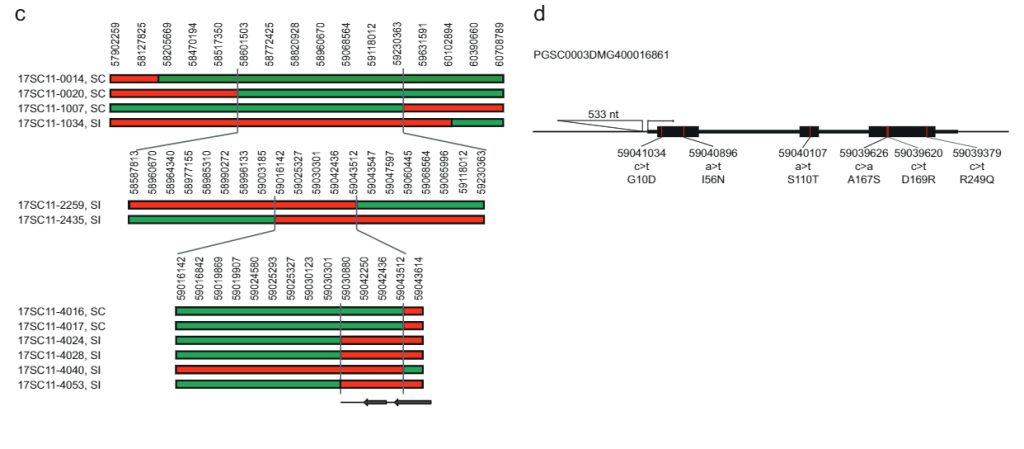
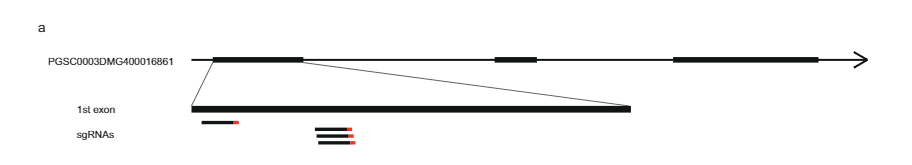
628 KB bitartean SLI 12SC17 populazioaren Sli-aleloa daraman 11. kromosoman tartea 169SC18 populazioan gainjarritako 12 KB-ko tarte txikiago batera murriztu zen, tarte horiek handiegiak ziren oraindik Sli-genea identifikatzeko. Hori dela eta, S/i duten tartea murriztea izan dugu helburu, baheketa birkonbinatzaile baten bidez. Errekonbinazioa duten landareak identifikatzea sli tartean, 1374 17SC11 landare genotipatu genituen KASP markatzaile bi hurbileko ertzean eta bi urruneko ertzean. Kanpoaldeko bi markatzaileen arteko birkonbinazioa duten 81 landare identifikatu ditugu eta mapaketa fin gehiago egiteko hautatu ditugu. Anbiguotasunik gabeko fenotipoak lortzeko, genotipo horiek modu begetatiboan hedatu ditugu eta genotipo bakoitzeko gutxienez bi klonetan fenotipatzea egin dugu. Tartean markatzaile gehiago zituzten 81 birkonbinatzaileak genotipatu genituen eta bost gene komentatuekin tartea 27.37 KBra murriztu zuten bi birkonbinatzaile informatibo identifikatu genituen (1. datu osagarriak).
Tartea gehiago murrizteko, populazio bereko beste 10165 plantula aztertu genituen 27.37 KB tarte honen inguruan lau markatzailerekin eta 12 birkonbinatzaile identifikatu genituen. Hauek gehiago genotipatu ziren tarte honetan beste 14 markatzailerekin eta bateragarritasun fenotipo argiak erakusten zituzten sei birkonbinatzaile informatibo identifikatu genituen. SC fenotipoa duten bi birkonbinatzaileek eta SI fenotipoa duen batek 27.37 KB-ko tartearen ertz distala berretsi dute, eta SI fenotipoa duten hiru birkonbinatzaileek, berriz, ertz proximal berri bat definitu zuten, tartea 12.6 kb-ra soilik murrizten duena, bi gene dituena, PGSC0003DMG400016861 eta PGSC0003DMG400016860 irudia. 1c).
Fenotipo autobateragarriaz arduratzen den gene hautagaia identifikatzeko, bi gene horien sekuentzia-aldakuntza aztertu dugu genoma osoko hainbat patata diploide-lerrotan (Datu osagarriak 2). Sekuentzia-aldakuntza hau lerro hauen SC/SI fenotipoekin alderatuz, SC-espezifikoak diren SNP eta INDELS guztiak identifikatu genituen (2. datu osagarriak). Ondoren, SNP ez-sinonimo guztiak eskuz identifikatu genituen eta aminoazidoen ordezkapenak Solanazeoetako antzeko proteinen ohikoak edo bakarrak diren zehaztu genuen. PGSC0003DMG400016861 gene hautagaiak SC-ren sei aminoazido-ordezkapen erakusten ditu eta, batez ere, hasierako kodoitik —533 bp-n kokatutako 108 bp txertaketa bat erakusten du, SC aleloak adierazpena aldatu duela SI aleloarekin alderatuta. Azterketa genetiko hauetan oinarrituta PGSC0003DMG400016861 dela hipotesia egin dugu. sli genea.
Sli polenean adierazten den hipotesia egiaztatzeko, 10 SI eta 10 SC patata genotipoetako polena ernatu genuen in vitro eta RNA atera genuen RNA sekuentziatzeko. Gainerako bi gene hautagaietatik, PGSC0003DMG400016861 gene hautagaia bakarrik adierazi zen, baina SC genotipoetako polenean soilik (Irudia. 2a). Gainera, Sli gene hautagai izateko heterozigotoak diren landareetan, Sli aleloa bakarrik adierazi zen. Interesgarria da, 12. kromosomako Sli locusetik gertu kokatutako polen bidez adierazitako beste geneek antzeko adierazpen-mailak erakutsi zituzten SC eta SI landareetan (Irudia. 2a). Hori dela eta, ondorioztatu dugu PGSC0003DMG400016861 genea bakarrik adierazten dela SC landareen polen-hodietan.
533 bp txertaketaren jatorria ikertzeko, NCBIn 533 bp sekuentziaren BLAST bilaketa egin dugu. Interesgarria da, Sli-ren txertatze espezifikoaren antzeko sekuentziak ohikoak dira sekuentziatutako S. tuberosum atxikipenak (Irud. 2b). Gainera, 533 bp txertaketak S-ko sekuentzia batekin homologia du. pennellii. S-ko segida erabiliz. pennellii BLAST kontsulta gisa antzeko sekuentziak aurkitu ditugu S-n. lycopersicum. urtean sekuentzien analisi filogenetikoa S. tuberosum, S. pennellii S. lycopersicum taldeak ditu S. pennellii sekuentziarekin batera S. lycopersicum eta bat S. tuberosum sekuentzia, hauek jatorri komun bat partekatzen dutela iradokiz (4a irudi osagarria). Txertaketa elementu transposagarri batetik (TE) eratorria dela planteatu genuen. 533 bp sekuentziatik dot-plot grafikoa sortu genuen eta sekuentziak miniaturazko alderantzizko errepikapenak zituela ikusi genuen (4b irudi osagarria). 533 bp-ko txertaketa BLAST-era bidali genuen landare MITE datu-basearen aurka, eta ondorioz, MITE familiako DTA_Sot42-ko hainbat hits. S. tuberosum15, 533 bp-ren txertaketa sustatzailean adieraziz sli hain zuzen ere, TE batetik dator (4c irudi osagarria).
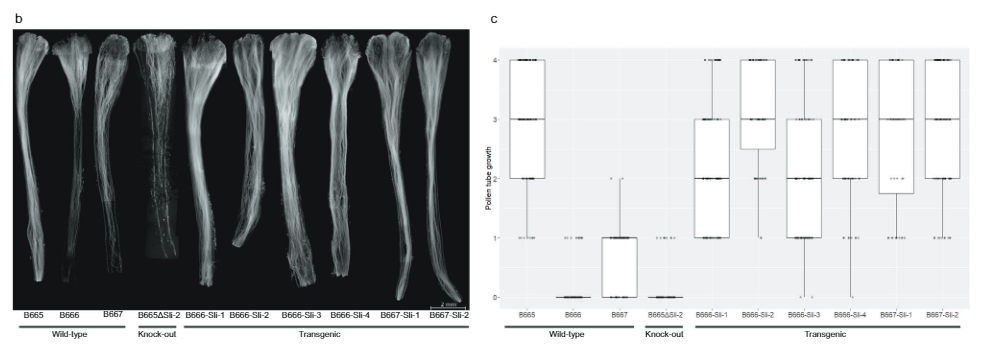
PGSC0003DMG400016861 benetan dela baieztatzeko sli, SC aleloaren exoiak dituen adierazpen-konstrukzio bat diseinatu dugu sli bere jatorrizko sustatzaile eta amaieraren artean (Fig. 3a) pBINPLUS bektorean (pBINPLUS-Sli). Eraikuntza hau erabili dugu SI genotipo bi 18SC12 populazio mapak eraldatzeko. SI B666 genotipotik eratorritako bost transgeniko independenteetako bi eta sei klon fenotipatu genituen, eta B667 SI genotipotik eratorritako hiru transgeniko.
Sei transgeniko independenteen klonek erraz jartzen dituzte baiak autopolinizazioan (3. datu osagarriak). Horrez gain, fluoreszentzia-mikroskopiak erakutsi zuen polena hori sli landare transgenikoak autoestiloetan sakontzen du eraldatu gabeko kontrolak baino (Irudia. 3b, c). Polen-hodiaren hazkundea lortu genuen 442 autopolinizaziotan sli transgenikoak eta 179 autopolinizazioa 0-4 eskalan eraldatu gabeko kontroletan. Polen-hodi gehienak obuluetara iristen ziren gehienetan sli transgenikoak, kontrolen zati oso txiki batekin alderatuta, PGSC0003DMG400016861 dela adieraziz. sli genea.
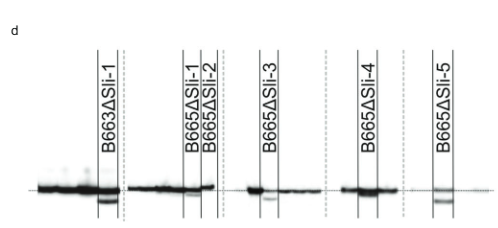
Ondoren, CRISPR-Cas9 eraikuntza diseinatu genuen lau gRNA kodetzen dituen PGSC0003DMG400016861 lehen exoira zuzenduta (pAGM: CRISPRASli, irudia. 3a). Bi SC genotipo (B665 eta B663) eraldatu genituen eraikuntza honekin eta 149 birsortzaile eraldatu lortu genituen. Ondoren, PAGE erabiliz zuzendutako exoia aztertu dugu CRISPR-Cas9-k eragindako INDELak identifikatzeko. Zoritxarrez, pAGM:CRISPRASli bektoreak eraginkortasun baxua zuen, 149 birsortzaileetatik seik baino ez zituzten INDELak erakusten. sli (Fig. 3d). CRISPR-Cas9 lerro hauetako bost heterozigotoak dira INDELentzat, baina lerro bat, B665ASli-2, homozigotoa da INDEL txiki baterako. Eraldatu gabeko B665ak auto-baiak erraz ezartzen dituen eta autopolen-hodiaren hazkuntza ona erakusten duen arren, behatutako 105 estilotan, B665ASli-2-k ez ditu baia ezartzen autopolinizazioan eta bere polena ezin da hazi ikusitako 78 estilotan (Irudia. 3b, c eta Datu osagarriak 3), PGSC0003DMG400016861 benetan dela frogatzen duten froga gehiago emanez. sli genea.
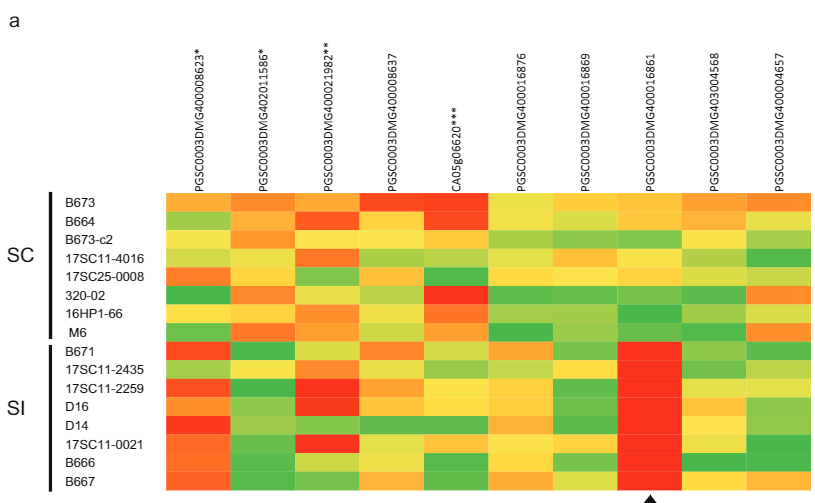
S-RNasan oinarritutako auto-bateraezintasun sistema gametofitikoetan, autoernalketa eragozten da polen-hodietan sartzen diren pistilo bidez adierazitako S-RNasek eta efektu zitotoxikoak eragiten dituzte auto-polenean edo bat datorren S-Locus F-kutxa (SLF) ez duen beste edozein polenean. ) proteina. Ernalketa gurutzatua S-RNasak ez diren S-RNasak ezagutu eta desintoxika ditzaketen polenak adierazitako SLF proteinek ahalbidetzen dute. S-alelo bakoitzak SLF anitz kodetzen ditu, horietako bakoitzak S-RNasa ezberdin bat antzeman dezake, eta elkarrekin patatan dauden S-RNasa gehienak antzeman ditzakete S-alelo berean kodetutako S-RNasa izan ezik. Sli-k PP2-B10 proteina F-kutxa bat kodetzen du, lectina-domeinu bati lotuta dagoen F-kutxa domeinu batez osatua. Lektina-domeinuek karbohidratoekin elkarreragin dutela eta proteina glikosilatuekin elkarreragiteko gai izan daitezke.16. Gainera, S-RNasak glikosilatuak daudela frogatu da17. Sli-ren SC aleloaren sustatzailean 533 bp txertatzeak polenean espresioa ahalbidetzen duela, non Sli-k auto S-RNasak lotu eta desintoxikatzeko gai den, auto-polen-hodiaren hazkuntza geldiaraztea eta, beraz, auto-bateragarritasuna galtzea eragiten du. Laimbeer-ek patatetan MITE jarduerari buruzko ikerketa zehatz batek aurkitu zuen eskualde genikoetatik hurbil dauden MITE txertatzeen % 2 geneen adierazpenaren aldaketekin lotuta zegoela.
Gainera, probatutako 1935 eskualde genikoetatik hurbil dauden hAT txertatzeetatik, 13k elkarturiko genearen goranzko erregulazioa eragin zuen, polenaren espresio espezifiko aldatua dela adieraziz. sli Izan ere, bere sustatzailean 533 bp txertatzeak eragin dezake18. Hala ere, ikerketa gehiago behar dira hipotesi honen baliozkotasuna zehazteko.
Aurretik, Clot et al-ek K-mer mapping segregatzaile bulked bat erabili zuten 333. kromosoman Sli kokatu behar den 12 kb-ko tartea identifikatzeko.19. Hemen, Sli locus-a F12 populazio batean 1. kromosomaren eskualde berean mapatu genuen eta baheketa birkonbinatzailea erabili genuen 12.6 gene dituen tartea 2 KBra murrizteko. Adierazpen-analisiak agerian utzi zuen gene horietako baten SC aleloa SC genotipoetako polenean espresuki adierazten dela. Azkenik, adierazpen transgenikoa eta CRISPR-Cas9-k eragindako knock-out erabiliz, PGSC0003DMG400016861 Sli dela behin betiko erakusten dugu. Laimbeer-ek egindako ikerketak MITEek hurbileko geneak ehunen modu espezifikoan gora erregula ditzaketela erakutsi zuen arren, ikerketa gehiago behar dira frogatzeko Sli sustatzailean MITEaren presentzia bere polenaren adierazpen espezifikoaren kausa dela.
Ikerketa honetan ikertutako materialetan (4. datu osagarriak), ezin izan genituen Sliren homozigositateari lotutako hilkortasunari buruzko aurreko txostenak baieztatu, baia ezartzeko gai ziren F2 landare bideragarriak aurkitu baititugu Slirentzat (1. datu osagarriak)12>20. Horrez gain, Solyntus endogamia-lerroaren genomaren sekuentziak, baita endogamia-lerroaren M6ak ere, bi lerro hauek Slirentzat homozigotoak direla erakusten dute, Slirentzat homozigositatea bera ez dela hilgarria adierazten du, nahiz eta oraindik posible den hilgarria izatea. arbaso batean Sli genetikoki lotuta dagoen aleloa birkonbinazioaren bidez kendu da genotipo hauetan21'22. Hala ere, ikerketa honetan sortutako datuetatik, ezin dugu baztertu F2 populazioan ikusten den segregazio-distortsioa fasean Sli-ren SI aleloari loturiko alelo hilgarri batek eragindakoa izatea. Oraindik ez dago argi Sli-k berak S-RNasak zuzenean ezagutu eta desintoxika ditzakeen ala ez. Gainera, ez dago argi Sli-k autobateragarritasuna sortzen duen ala ez S-locus genotipo guztietan. Baliteke S-alelo batzuen funtzioa Slik ezin izatea inhibitzea. Galdera hau konpontzeko ikerketa gehiago behar dira.
Sli-ren identifikazioak patata diploidea erabiliz endogamian oinarritutako hazkuntza hibridoa ahalbidetzen duen arren, beste oztopo batzuk geratzen dira. Lehenik eta behin, esanguratsuena, patata diploideak endogamiaren depresioa jasaten du, eta horrek indarra eta ugalkortasuna murrizten ditu endogamian. Patata-lerro diploideen autoernalketa jarraituz alelo kaltegarrien garbiketa metodo eraginkorra da endogamiaren depresioa murrizteko eta dagoeneko patata-lerro konparatiboki indartsu eta emankorrak sortu dira.2'23-25. Bigarrenik, ikerketa honetan erabilitako Sli emailea, DS, S batetik eratorria da. chacoense atxikipena, S.-ren alelo kaltegarrien lotura-errestaketaren arazoak sor ditzakeela. chacoense. Solynta-ren hazkuntza diploide programan, ez dugu ageriko arazorik ikusten S. chacoense-tik datozen alelo kaltegarriengatik. Gainera, auto-bateragarritasunari buruzko azken ikerketa batek agerian utzi zuen SC-ko espezifikoak k-merak dagoeneko presente daudela hainbat kulture tetraploidetan, eta bide bat eskaintzen du balizko lotura-arrastaketa hori guztiz saihesteko, kultibo horietatik sortutako dihaploideak Sli emaile gisa erabiliz.19.
Metodoak
Landare-materialak. Erabilitako landare-material guztiak 4. datu osagarrietan ageri dira
Berotegi-baldintzak. Landare guztiak berotu egiten ziren negutegietan, tenperatura 14 °C-tik behera jaisten zenean, eta leihoak irekiz hozten ziren tenperatura 19 °C-tik gora igo zenean. Argi artifizialak argi naturala osatzen zuen argiaren intentsitatea 85 W/M2-tik behera jaisten zenean. Landareak Lentse Potgrond-eko patata-substratu nahasketa berezi batean hazi ziren (Lentse Potgrond BV, Katwijk, Herbehereak). Erabilitako substratu-nahasketa zohikatz-nahasketaz osatuta dago, ura orekatuta hartzeko, askapen moteleko oinarrizko ongarriz eta karez, beharrezko pH-maila bermatzeko. Substratu nahasketa 20:20:20 Nitrogenoa: Fosforoa:Potasioa 1.5eko eroankortasun elektrikoarekin (EC) disoluzioarekin ernaldu zen.
Auto-bateragarritasunaren ebaluazioa. Loreak eta begiak astean behin zenbatu ziren eta indarra hilean behin neurtzen zen 1etik 9ra bitarteko eskalan, 1 landare oso kementsu bat izanik, eta 9 landare oso indartsua izanik. Landare bateko lore anitzetako polena Eppendorf hodi batean bildu eta berehala erabili zen lore berdinetan autopolinizaziorako, gehienez 10 lore astean landare bakoitzeko. Baia bakoitzeko gutxienez 35 hazi dituzten bi baia baino gehiago ezartzen dituzten landareak auto-bateragarri gisa sailkatu dira. Emeen emankortasuna zehazteko, landareak gutxienez zerikusirik ez zuten hiru genotipotako polen bulkedarekin polinizatu ziren. Gutxienez 10 autopolinizazioren ondoren auto-baia ezarri ez zuten landareak, baina baia ontziratu bat gutxienez ezarri zuten eta autopolinizazio-estiloen analisi mikroskopikoetan polen emankorra erakutsi zuten auto-bateraezin gisa sailkatu ziren. Baia eta hazi-multzoaren datuak erabakigarriak ez ziren 40 genotipotarako (17SC11: n = 14, 18SC11: n = 7, 18SC12: n = 19), sailkapen fenotipikoa estiloen bidez autopolenaren hodiaren hazkundean oinarritzen zen (1. datu osagarrian adierazita).
Estilo-irudiak. Polen-hodiaren hazkundea ikusteko, polinizatutako estiloak polinizazioaren ondoren 24-48 ordura kendu ziren eta, ondoren, 3:1 etanol: azido azetikoan finkatu ziren gutxienez 24 orduz. Ondoren, estiloak 8M NaOHn mazeratu ziren 10 minutuz 65 °C-tan eta birritan garbitu ziren ur deionizatuarekin. Estiloak mikroskopiako diapositibetan jarri eta 2-5 minutuz tindatu ziren % 0.1 anilina urdina erabiliz (Carl Roth GmbH) 0.1MK-n.4P2O7 (pH = 7), gero glizerlean zapaldu estalontzi baten bidez eta Zeiss Axiolab fluoreszentzia mikroskopioa erabiliz behatu 01 iragazki-multzoa erabiliz (BP 365/12, FT 395 eta LP 397). Estilo guztiak behatu eta puntuatu ziren bi parametro erabiliz: (1) estiloan sartzerik sakonena, sartze maximoaren ehunekoan adierazita, (2) polen-hodien % sartzerik sakonenera iristen zen. Ondoren, ehuneko hauek 0-4 eskala bihurtu genituen, non polen-hodirik obulutegira iristen ez ziren estiloek 0ko puntuazioa lortu zuten, polen-hodien % 0 artean 25eko puntuazioa lortu zuten estiloek, estiloek 1 artean. eta polen-hodien % 25 obulutegira iristen zen 50 puntuazioa lortu zuten, polen-hodien % 2 eta % 50 artean obulutegira iristen zen estiloek 75ko puntuazioa lortu zuten eta polen-hodien % 3 baino gehiago obulutegira iristen ziren estiloek. 75ko puntuazioa.
Irudia eskuratzea. Aukeratutako estiloak 01 iragazki-multzoa duen Zeiss Axiophot mikroskopio batekin irudikatu dira, Zeiss AxioCam ICc 5 erabiliz. Irudiak Zeiss Zen 2.3 (edizio urdina) software paketearekin egin dira. Eskuratzean, ezarpenak egokitu ziren atzeko planoa minimizatzeko. Estiloak x5 helburua erabiliz irudikatu ziren eta TIFF fitxategi gisa gorde ziren 2464 x 2056 pixeleko bereizmenarekin 24 biteko sakonerarekin. Gero, zortzi irudi bereizi muntatu ziren Panavue irudien muntatzailea erabiliz. Muntatutako estiloen kontrastea eta distira egokitu ziren irudiak sortzeko. 1a eta 3c.
DNA erauztea. Populazioen mapak KASP aztertzeko, hosto-laginak VHLGenetics-era (Wageningen, Herbehereak) bidali ziren DNA erauzteko sbeadex™ kitak erabiliz (LGC Genomics GmbH, Berlin, Alemania) fabrikatzaileak emandako protokoloaren arabera.
KASP azterketa. Konpetitive alelo-specific PCR (KASP™) analisia VHLGenetics-ek (Wageningen, Herbehereak) egin zuen gure materialan bereizten diren SNPetarako espezifikoak izateko diseinatutako KASP entseguak erabiliz. KASP entseguak fabrikatzaileak (LGC Genomics GmbH, Berlin, Alemania) emandako protokoloaren arabera egin ziren. KASP entseguen emaitzak SNPviewer erabiliz bistaratu ziren (lgcgroup.com/products/genotyping-software/snpviewer helbidean) bereizketa eta genotipo dei zuzena baieztatzeko.
Lotura-analisia. Emakumezko guraso auto-bateragarrien haplotipoak genotipoaren datuetatik berreraiki ziren SNP ezberdinen arteko birkonbinazio-tasak aztertuz. Datu hauek SNP deiak "axb" formatuan bihurtzeko erabili ziren, non "a" haplotipoa Sli-ren alelo auto-bateragarriari lotuta dagoen eta "b" haplotipoa Sli-ren auto-bateraezina den alelo bati lotuta dagoen bitartean. Lotura-mapak Joinmap 4.1 erabiliz sortu ziren26 DH populazio motarekin eta ezarpen lehenetsiekin.
QTL mapak. Fenotipoaren datuak zenbakizko ezaugarri bihurtu ziren, 1 auto-bateragarria den genotipo bakoitzari, 0 auto-bateraezina den genotipo bakoitzari eta * bateragarritasuna zehaztu ezin zen genotipoei. QTL mapaketa MapQTL-n tarte-mapea erabiliz egin da27. MapQTL-ren irteerak QTL grafikoak sortzeko erabili ziren Mapchart 2.3-rekin28.
Analisi bioinformatikoa. Hasierako 27.37 kb-ko tartean gene-eredu zuzenak identifikatzeko, DM4.04 erreferentziako genomaren bi gene-anotazio bereizi ikertu ditugu, PGSC-en eta ITAG-en. Ikus, halaber, Hirsch et al.29. Oharpenen zuzentasuna baieztatzeko, BLASTp bilaketak egin ditugu bi oharretatik aurreikusitako proteina-sekuentziekin. BLASTp bilaketako arrakasta onenak gure kontsultarekin alderatuz, aurreikusitako proteina-sekuentzian ohartatutako exoi eta domeinu guztiak patata eta beste landare-espezie batzuen antzeko proteinak onartzen ote ziren zehaztu genuen. Gainera, publikoki eskuragarri dauden RNA-seq liburutegiak SPUD DB-n (solanaceae.plantbiology.msu.edu/cgi-bin/gbrowse/potato/ helbidean eskuragarri) eta NCBI genomaren datu-ikustailean (eskuragarri ncbi.nlm.nih.gov/genome/gdv helbidean). /browser/) erabili ziren ustezko exoiak adierazpen frogarik ote zuten zehazteko. Batera, bi hurbilketa hauek gene-ereduen introi-exoien egiturak balioztatzeko aukera eman ziguten bi oharpenetan, eta ondorioz, gene-ereduen isoforma bat edo gehiagoren aukera informatua izan zen kasuan kasuko genea irudikatzeko. Planteamendu horietan oinarrituta, PGSC0003DMG400016862 gene hautagaia ziurrenik partziala eta hutsalki adierazia eta analisi gehiagoetatik baztertua izan zen. Sotub12g029970 gene-eredua zuzentzat jo zen, eta bere PGSC parekoa PGSC0003DMG400016860 litekeena da moztuta egotea. Neurri handi batean izendatutako tartetik kanpo kokatzen denez, eta SC eta SI landareen arteko aminoazido-ordezkapen garrantzitsurik ez zelako identifikatu, gene hau analisi gehiagoetatik baztertu zen.
Aldakuntza-analisia. Auto-bateragarriak diren genotipoetarako espezifikoak diren 27.37 kb-ko mutazioak identifikatzeko konfiantza handiko SNP guztiak (3. datu osagarriak) zehaztu ziren (1) homozigotoak zirela DS, 17SC100-18 eta 17SC100-2 (hirurak homozigotoak direlako). -ren SC aleloa Sli (Sli/Sli')'), (2) homozigotoa desberdina D16-n (D16 homozigotoa delako Sli-ren SI alelorako (sli/sli)), eta (3) heterozigotoa bai 16HP1-66 eta 17SC25-8-n (biak heterozigotoak direlako SC alelorako Sli (Sli). /sli)). Sekuentzia alelikoa de novo muntaketaz lortu zen SPAdes 3.11.1 bertsioa erabiliz30 Goian zerrendatutako landareen 150 nt parekatuko Illumina datuen (25-30X gutxi gorabehera sekuentziazio-sakonera). Sortutako kontigak DM erreferentziara lerrokatu ziren (minimap2 2.1 bertsioa erabiliz) eta 27 kb-ra fidagarritasunez lerrokatzen zirenentzat iragazi ziren. Lerrokaturiko kontig horietatik, DM4.03-ren aldakuntza zuzenean kuantifikatu zen (mileup azpierrutinek eta bcftools-en deia, 1.9 bertsioa erabiliz) eta Variant Call Format (VCF) zerrendatu zen.
Aminoazidoen aldaketaren analisia. SC-ren mutazio espezifikoen zerrenda honetatik, SNP ez-sinonimo guztiak identifikatu ziren izendatutako kode-exoiekin gainjarriz. DM edo SI sekuentziarekiko aminoazidoen aldaketak zerrendatu ziren. Aminoazidoen aldaketa bereziak identifikatu ziren proteina-sekuentzia erabiliz BLASTp bilaketak eginez eta 100 BLASTp arrakasta nagusien bidez sekuentzia anitz lerrokatzea eginez.
Eskualde sustatzaile eta amaierako aldakuntza. Eskualde sustatzailea hasierako kodoiaren gorako sekuentzia izateko aukeratu zen, gehienez 1500 nt-ko gorako genearen sekuentzia kodetzailea izan arte. Eskualde sustatzaileetan aldakuntza ikaragarria aurkitu zen 27.37 kb-ko tartean, eta deigarrienak hamarnaka eta ehunka nukleotidoko luzera duten hainbat ezabaketa eta txertaketa izan ziren. Sli tartearen aldakuntza guztiak, DMarekiko, lortu ziren, sustatzaile/upstream eskualdearena eta amaiera/downstream eskualdearena barne.
Polena eskuratzea eta ernetzea. Irudian zerrendatutako genotipoetako polena. 2a hortzetako eskuila elektroniko baten bidez irekitako loreak bibratuz eta 1.5 ml-ko Eppendorf hodietan polena bilduz lortu zen. Eskuratu ondoren, polena lehortu zen, irekitako Eppendorf hodiak polenarekin airez itxitako kutxa batean gordez silize gela 24 orduz giro-tenperaturan. Ondoren, polena -20 °C-tan gordetzen zen gehiago erabili arte.
Polena ernetzen zen 2.5 mg polen lehor 5 ml medio likidotan (% 9 (w/v) sakarosa, 50 mg/l azido borikoa, 73.5 mg/l CaCly2H) esekituta.2O, 118 mg/l Ca (NO3)24H2O, 123 mg/l MgSO.4VH2O) 3.5 cm-ko diametroko Petri plaketan parafilmez zigilatua. Polena Petri plateretan ernetzen utzi zen 24 orduz ilunpetan, giro-tenperaturan astindutako inkubagailu batean eta 125 RPM-n astinduz. Gero, ernetutako polena zuen medio likidoa arretaz pipetatu zen 2 ml Eppendorf hodietan, irekidura-tamaina handitzeko aldatu ziren pipeta-puntak erabiliz, polen-hodiak ez kaltetzeko. Ondoren, Eppendorf-eko hodiak 600xg-tan zentrifugatu ziren 1 minutuz eta medioa arretaz kendu zen pipetatuz. Pelleta eta gainerako medio batzuk berehala izoztu ziren nitrogeno likidoan, altzairu herdoilgaitzezko bi ale gehitu ziren (2 mm-ko diametroa) eta laginak TissueLyser II (Qiagen GmbH, Hilden, Alemania) erabiliz ehotu ziren 20 Hz-tan 1 minutuz.
RNA erauzketa eta sekuentziazioa. Buffer RLT (Qiagen GmbH) ehotutako polen laginei gehitu zitzaien laginak izoztuta geratzen zirela ziurtatuz. Ondoren, RNA erauzketa RNeasy mini kitarekin egin zen fabrikatzailearen protokoloaren arabera (Qiagen GmbH, Hilden, Alemania). 250-300 bp-ko txertatze-tamainako cDNA liburutegiak 150nt pareka-muturreko irakurketa gisa sekuentziatu ziren, lagin bakoitzeko 30-42 milioi irakurketa-pare emanez (Novogene, Cambridge, Erresuma Batua).
RNA-seq beste datu multzo batzuk. Adierazpen-mailen (ehunen espezifikoen) ikuspegi orokorra sortzeko, ORGANIMO gisa etiketatutako RNA-seq sekuentziatutako RNA-sekuentziadun datu multzo guztiak "Sola-num tuberosum" domeinu publikotik deskargatu ziren (NCBI-SRA, 2018/17/13 data), guztira 441 parekatuta fastq datu multzoak. 441 datu-multzo publiko horietatik, 3 estilo-ehunetatik (SRR7402817-SRR7402819) eta beste guztiak polenetik kanpoko hainbat ehun, garapen-fase eta landareen atxikipenetatik sortu ziren.
Solyntus erreferentziako muntaia. Adierazpen-analisiak egiteko, Solyntus erreferentzia-lerro homozigotoaren zirriborroa (1.0 bertsioa, deskargatu daiteke). www.plantbreeding.wur.nl/Solyntus/) erreferentziazko genoma gisa erabili zen. Solyntus, funtsean, barietate homozigotoa da, Solyntaren hazkuntza-programaren baitan sortutakoa21. Azterketa honetako mapatze-tarteak DM v4.03 genomaren muntaiatik ondorioztatu ziren31 Solyntus 1.0 genomaren muntaketari oinarrizko antzekotasun-bilaketen bidez (BLASTn eta bedtools erabiliz) kokatuko den (Solyntus 1.0 genomaren muntaiaren koordenatuak) 53532708-53954293 (I. tartea, 421.6kb < —628.9) (tartea) , 53683239. kb< — 53867377 kb), 184.1-168.7 (III tartea, 53731620 kb< —53763003 kb) eta 31.4-27.4 (IV tartea, 53753977 kb < —53763003 kb), hurrenez hurren. Parentesi artean segidako mapa-tartearen zenbakia [Solyntus 9.0 koordenatuak], tamaina Solyntus-12.6-n eta tamaina DM-1.0/1.0-n daude, hurrenez hurren. Tarte guztiak ST4.03ch4.04_RaGOO kromosoman daude (4.03. kromosoma izanik) eta ez dute hutsune bakar bat Solyntus 12 muntaian. Tarte-tamainaren aldakuntza dagokion DM sekuentzian hutsune ugarik (N) eta bi genomaren arteko aldakuntza handiek eragiten dute. DM genomaren (DM-12/1.0) dagozkion tarteak: I. tartea: chr4.03:4.04-12, II. tartea: chr58601503:59230363-12; III tartea: 58962004-59130723; IV tartea: chr59016142:59043512-12.
Solyntus 1.0-n geneen oharpena hiru gene katalogo ezberdinetatik ondorioztatu zen (patata DM4.03, ITAG4.0 Tomato Genomaren Oharra, 6ko irailaren 2019an).32, eta Piper-v. 1.5533), GeMoMa erabiliz (v1.6.1) Solytus muntaian mapatu ziren. Hau geneen katalogo indibidualetako akatsak konpentsatzeko eta gene eta/edo adierazitako loci posibleen existentziaz gure kontzientzia maximizatzeko egin zen.
RNA-seq irakurketa-mapaketa eta transkripzio ugaritasun kuantikoakfikazioa. 5 SC, 3 SI eta RNA-seq publikoko 441 datu multzo guztiak Solyntus erreferentziako genomarekin mapatu ziren hisat2 erabiliz (2.1.0 bertsioa). GeMoMa erabiliz lortutako gene hibridoen katalogoa StringTie (2.1.1 bertsioa) erabiliz transkripzioz gidatutako ugaritasuna kalkulatzeko erabili zen -t -c 5 -f 0.05 -G ezarpenekin eta GeMoMa kateatu Solyntus1.0 gff fitxategi batekin. Behatutako adierazpen guztiak 500 kb-ko tarte batean sli Lokus zentro gisa ebaluatu zen, tarte horretan guztira 90 (ondorioztutako) gene-loku kokatzen dira. Gene loci hauetatik kanpo SC laginetan adierazpen nabarmenik ez dagoela baieztatu dugu. 500 kb-ko tartean, gerora gene hautagaien kopuru txikiagoa adierazi genuen goian definitu den bezala gure mapatze-tarteekin gurutzatzean.
Withfihaplotipo-espezieen rmazioafic adierazpena. 90 kb-ko tartean adierazitako 500 lokuetatik, 8 bakarrik adierazi ziren 20 FPKM-ko atalasearen gainetik hautatutako SC/SI lagin guztietan. Gune hauek haplotipo espezifikoak (Sli edo sli) espresio-mailaren desberdintasunak neurtzeko erabili ditugu. Hautatutako adierazpen-atalasak irakurketa-sakonera nahikoa ahalbidetu zuen, azkenean eta modu fidagarrian adierazpena 2 haplotipotan (gehienez) fasekatzeko. PSC locus berarekin batera (SI landareetan adierazpenik ez duena), 8 + 1 loci hauek haplotipatu ziren 8 laginetako bakoitzean (SAMtools faseko 1.7 bertsioa, ezarpen lehenetsiak). Ondorioz, fastq fitxategi haplotipatuak (parekatuak) de novo muntatu ziren SPAdes erabiliz (3.11.1 bertsioa). Ondorioz, kontigak ugaritasun zabalerako eta ustezko luzera osoko mRNAak iragazi ziren, adierazitako isoforma nagusiari dagozkionak (haplotipatua). Zenbait kasutan, honek alternatiba splizatutako isoformak kendu zituen, eta horietako bat ere ez zen irakurketa zabalek garrantzi biologiko nabaria zutenik onartzen. Haplotipatutako mRNA sekuentzia hauen aldakuntza erabili zen (des)baieztatzeko haplotipo bat edo biak dagozkien loku/lagin bakoitzean adierazten ziren.
Diseinua sli adierazpenaren eraikuntza. Sli landare emailearen DS sekuentzia erabili dugu Sli adierazpen kasetea diseinatzeko. Berezko adierazpena ahalbidetzeko PSC, azido nukleikoen sekuentzia bat eraiki dugu sustatzaile natiboa (1563 bp hasierako kodoiaren gora), hiru exoiak eta amaitzaile natiboa (740 bp geldiuneko kodoitik behera). Horrela, bi introiak kendu ziren PSC DS landare emailearen genea. Genscript-ek (Genscript Biotech, Leiden, Herbehereak) sintetizatu eta pBINPLUS-en klonatu zuen sekuentzia hau. duen bektoreari erreferentzia egiten diogu sli txertatu pBINPLUS-Sli gisa.
CRISPRren eraikuntza-Cas9 bektorea. DM0003-n PGSC400016861DMG4.03 sekuentzian oinarritutako lau gRNA diseinatu genituen SC eta SI aleloen arteko aldakuntzarik ez zegoen tokietan. Gida egokiak aukeratzeko eta bektorearen eraikuntzarako, Santillan Martinez et al-ek deskribatutako metodoa erabili dugu.34. Laburbilduz, lau sgRNA hautatu ziren Liang et al-ek deskribatutako jarraibideen arabera.35. CC-Top CRISPR/Cas9 xede iragartzeko tresna erabili zen sgRNA zerrenda bat sortzeko36, tolestea Mfold web zerbitzaria erabiliz ebaluatu da37, eta sgRNA-en jarduera sgRNA puntuatzailea erabiliz aurreikusi zen38. Gida hauek aukeratu eta erabili ziren pAGM bektorea eraikitzeko:CRISPRASli: exon5.1T01 (ATTTCATCCGCGATCTCTCGGGG), exon5.1T04 (GATTTCA TCCGCGATCTCTCGGG), exon5.1T06 (TATTTCCTATTGCTACCAGAAGG) eta exon5.1TGCGATCTCTCGGG. CRISPR konstrukzioa Addgenetik lortutako plasmidoen bidez sintetizatu zen ondoren: pICH07 (anplifikaziorako txantiloia); pICSL86966 (01009. mailako plasmidoa); pICH0, pICH47751, pICH47761, pICH47772 eta pICH47781 (47732. mailako plasmidoak); pICH1 (lau gidetarako estekatzailea); eta pAGM41822 (4723. mailako bektore bitarra). Plasmidoa erabiliz klonatu zen E. coli DH5a eta araztutako plasmidoa sekuentziatzeko PDS5843 (TTTGTGATGCTCGTCAGGGG), PDS8535 (CCCGAGAATTATGCAGCATT TT) PDS8536 (TCATCAGTCAATTACGGGGCT) eta AL717 (GCTTGGCATC AGACAAACCGG) osagai guztien presentzia eta orientazio zuzena (Cas9g) orientazio zuzena baieztatzeko lehengaiak erabiliz bidali ziren.
pBINPLUS-Sli eta pAGMzCRISPR-en eraldaketaASli bektorea sartu Agrobacterium tumefaciens. pBINPLUS-Sli bihurtu dugu A. tumefaciens iragazi AGL0 eta pAGM:CRISPRASli A sartu. tumefaciens AGL0 eta AGL1 tentsioak elektroporazio-protokolo bat erabiliz. 40 pl AGL0 zelula konpetente hartu eta 110 pl izotz miliQ ur gehitu ditugu. Nahasketa honen 50 pl-ko pipeta egin genuen izotz gainean aldez aurretik hoztutako Eppendorf hodietan eta plasmidoaren 1 pl gehitu genituen. Zelulak izotzetan utzi genituen 15 minutuz eta zelulak aurrez hoztutako elektroporazio kubetetara transferitu genituen. Nahasketak Micropulser™ batekin elektroporatu genituen (Bio-Rad Laboratories, Vee-nendaal, Herbehereak) Ec1 programa erabiliz (1.8 kV, 0.1 cm-ko kubeta). 1 ml LB gehitu eta zelulak 3 orduz inkubatu genituen 28 °C-tan eta 200 RPM-ko astingailu batean. Ondoren, Rifampicina (100 pg/ml) eta Kanamizina (50 pg/ml) dituzten LB agar plakak eraldaketa-kulturarekin inokulatu ditugu. Hautatutako kolonia guztiek bektore zuzena zutela baieztatu zen.
Patataren genotipoen eraldaketa. B666 eta B667 genotipoak pBINPLUS-Sli-rekin eta B663 eta B665 genotipoak pAGM:CRISPRASli bektorearekin eraldatu ditugu Visser-ek deskribatutako zurtoin-explant metodoa erabiliz.39. Laburbilduz, in vitro hazitako genotipoetatik lortu ziren entrenode esplanteak eta R3B medioa zuten Petri plaketan jarri ziren 2 ml PACM medioarekin. Hurrengo egunean, 50 h-ko 48 ml Agrobacteriuma kulturak zentrifugatu eta 75 ml LB-tan berriro esekitzen ziren. Gero, barne-ondoko esplanteak urpean murgildu ziren Agrobacteriuma esekidura 5 minutuz, iragazkian lehortu eta berriro R3B medioa duten Petri plaketan jarri. 48 orduko inkubazioaren ondoren, esplanteak MS20 zuten Petri plaketara transferitu ziren antibiotikoekin eta hazkuntza-ganbera batean jarri ziren kimuak birsortzeko. Birsortu ondoren, kimuak cefotaxime (20 pg/ml), vancomycin (200 pg/ml) eta kanamizina (200 pg/ml) zituzten MS100 euskarrietan hazi ziren. Kimuak nahikoa luzera iristen zirenean, mozketak egin eta MS20n hazi ziren antibiotikorik gabe. Gutxienez bi aste MS20n antibiotikorik gabe hazi ondoren, landareak negutegian landatu ziren.
Ploidia analisia. Landare transgenikoen ploidia eta eraldatu gabeko kontrolak fluxu-zitometria erabiliz zehaztu ziren Plant Cytometry Services-ek (Didam, Herbehereak). Erregeneratzaile tetraploide guztiak baztertu ziren.
CRISPR-ren ORRIALDEA analisia-Cas9-k eragindako mutazioak. DNA erauzketa, PCR eta PAGE analisiak Limgroup-ek (Horst, Herbehereak) egin zituen. CRISPR-Cas9-ren xede den eskualdea anplifikatzeko abiarazle hauek erabili ziren: Aurrerako abiarazlea: CTATTTCCTATTGCTACCAG, alderantzizko abiarazlea: AAACTTTACCCAAAT AACGTC. PCR produktuen etiketatzea M13 isatsarekin (primer sekuentzia: TGTAAAACGACGGCCAGTAAACTTTAC CCAAATAACGTC) eta 700 IRDye edo 800 IRDye etiketatutako M13 lehengaia PCR nahasketara gehituz lortu zen. Lortutako PCR produktuak PAGEn aztertu ziren Li-cor sistema erabiliz. CRISPR-Cas9-k eragindako mutaziorik gabeko lerro gehienetako PCR produktuak gel-irudietatik kendu ziren irudia sortzeko. 3d (ebakidurak marra etenekin adierazita).
533 bp txertaketaren analisi filogenetikoa. 533 bp txertaketaren sekuentzia BLASTn erabiliz aztertu da NCBI webgunean. 30 hit onenak, bertan dagoen txertaketa barne sli Solyntus-en, MegAlign Pro 17-n (DNASTAR) deskargatu eta lerrokatu ziren MUSCLE ezarpen lehenetsiekin. Zuhaitzek ezarpen lehenetsiekin auzokideen batzeko algoritmoa erabiliz sortu ziren.
Txostenaren laburpena. Ikerketa-diseinuari buruzko informazio gehiago eskuragarri dago artikulu honi lotutako Nature Research Reporting Summary-n.
Datuen erabilgarritasuna
Solyntus genomaren sekuentzia eta sekuentzia gordinaren irakurketak NCBIn eskuragarri daude atxikipenean PRJNA631911. Solyntus genomaren muntaia eta oharpen-fitxategiak WUR-en daude eskuragarri.https://www.plantbreeding.wur.nl/Solyntus/]. Ernetutako polenaren RNA sekuentziatzeko datuak eskura daitezke NCBI irakurketa laburreko artxiboan eskuragai PRJNA713577. Beste datu batzuk iturburu-datuen fitxategian daude eskuragarri edo eskatuta egongo dira eskuragarri. Iturburuko datuak dokumentu honekin batera ematen dira.
Jasotakoa: 22eko urtarrilaren 2021a; Onartua: 8eko ekainaren 2021a;
Linean argitaratua: 06 uztaila 2021
Erreferentziak
- 1. Duvick, DN Ugaltzearen ekarpena artoaren aurrerapenak emateko (Zea maiatzak L.). Adv. Agron. 86, 83-145 (2005).
- 2. Lindhout, P. et al. F1 hazi-patata hibridoaren hazkuntzarantz. Patata Erres. 54, 301-312 (2011).
- 3. Jansky, SH et al. Patata berrasmatzea lerroetan oinarritutako uzta diploide gisa. Laborantza Sci. 56, 1412-1422 (2016).
- 4. Ye, M. et al. S-RNasaren knockout-aren bidez patata diploide auto-bateragarria sortzea. Nat. Landareak 4, 651-654 (2018).
- 5. Enciso-Rodriguez, F. et al. CRISPR-cas9 erabiliz patata diploidean auto-bateraezintasuna gainditzea. Aurrealdea. Landare zientzia. 10, 1-12 (2019).
- 6. Su, Y. et al. Kontrako erresistentziarako geneen introgresioa Phytophthora infestans patata diploidean. Am. J. Patata Res. 97, 33-42 (2020).
- 7. Dzidzienyo, DK, Bryan, GJ, Wilde, G. & Robbins, TP S-RNase aleloen aniztasun alelikoa patata diploideetan. Theor. Apl. Genet. 129, 1985-2001 (2016).
- 8. McClure, B., Cruz-Garcia, F. & Romero, C. S-RNasan oinarritutako sistemetan bateragarritasuna eta bateraezintasuna. Ann. Bot. 108, 647-658 (2011).
- 9. Kubo, K. et al. S-RNasan oinarritutako auto-bateraezintasunean oinarritutako ez-auto-ezagutze sistema kolaboratiboa. Zientzia: 330, 796-799 (2010).
- 10. De Jong, H. & Rowe, PR Endogamia landatutako patata diploideetan. Patata Erres. 14, 74-83 (1971).
- 11. Hermsen, JGT & Olsder, J. Genetics of self-compatibility in dihaploids of Solanum tuberosum L. 1. Bi dihaploide auto-bateragarriren ugaltze-jokabidea. Eufitika 25, 597-607 (1976).
- 12. Hosaka, K. & Hanneman, RE Jr. Auto-bateragarritasunaren genetika patata diploide basati-espezie autoincompatible batean Solanum chacoense. 1. S locus inhibitor (Sli) gene baten detekzioa. Eufitika 99, 191-197 (1998).
- 13. Hosaka, K. & Hanneman, RE Jr. Auto-bateragarritasunaren genetika patata diploide basati-espezie autoincompatible batean Solanum chacoense. 2. S locus inhibitor (Sli) gene bat patataren genoman lokalizazioa DNA markatzaileak erabiliz. Eufitika 103, 265-271 (1998).
- 14. Birhman, RK & Hosaka, K. S-locus inhibitzaile (Sli) gene bat erabiliz patata diploideen endogamien progenieen ekoizpena eta haien karakterizazioa. Genoma 502, 495-502 (2000).
- 15. Chen, J., Hu, Q., Zhang, Y., Lu, C. & Kuang, H. P-MITE: landareen miniaturazko elementu transposagarrientzako datu-basea. Azido nukleikoak. 42, 1176-1181 (2014).
- 16. Stefanowicz, K., Lannoo, N. & Van Damme, EJM Plant F-box proteins- bizitzaren eta heriotzaren arteko epaileak. Kritikoa. Errev. Landare Sci. 34, 523-552 (2015).
- 17. Liu, B., Morse, D. & Cappadocia, M. S-RNasen glikosilazioa Solanum chacoense-n polenaren errefusaren atalaseetan eragin dezake. J. Exp. Bot. 59, 545-552 (2008).
- 18. Laimbeer, FPE Patataren genomika hiru modu: tuberkuluetako endoreduplicazioaren kuantifikazioa, transposoien lur-eremuan barrena eta loreen kolorearen erregulazioa argitzea. http://hdl.handle.net/10919/84480 (2018).
- 19. Clot, CR et al. Sli-n oinarritutako autobateragarritasunaren jatorria eta hedatuta dagoena patatan. Theor. Apl. Genet. https://doi.org/10.1007/s00122-020-03627-8 (2020).
- 20. Endelman, J., Jansky, SH, Butler, N. & Christensen, G. Potato Association of America-ren 12 urteko txostena patata kromosomako alelo hilgarri errezesiboaren froga genetikoa. Am. J. Patata Res. 96, 331 (2019).
- 21. van Lieshout, N. et al. Solyntus, patataren (Solanum tuberosum) erreferentzia oso ondoko genoma berria. G3 Geneak Genomak Genet. 10, 3489-3495 (2020).
- 22. Leisner, CP et al. M6-ren genoma sekuentzia, glikoalkaloide altuak ekoizten dituzten tuberkuluak dituzten patata-espeziearen klona diploidea Solanum chacoense, hondar heterozigositatea agerian uzten du. Landare J. 1967, 562-570 (2018).
- 23. Peterson, BA et al. Infinium 8303 patata nukleotido bakarreko polimorfismo arrayarekin aztertutako patata diploideen populazio landu batean auto-ernaltasuna. Landareen Genoma https://doi.org/10.3835/plantgenome2016.01.0003 (2016).
- 24. Lian, Q. et al. Patataren poliploidizazioan mutazio kaltegarriak eskuratzea. J. Integr. Landare Biol. 61, 7-11 (2019).
- 25. van Lieshout, N. et al. Solyntus, patataren erreferentzia oso ondoko genoma berria (Solanum tuberosum). G3 Geneak Genomak Genet. 631911, g3.401550.2020 (2020).
- 26. Van Ooijen, JW BatuMap®4, Populazio Esperimentaletan Lotura Genetikoen Mapak Kalkulatzeko Softwarea liburukia 33 (Kyazma BV, 2006).
- 27. van Ooijen, JW Espezie autogamoetan ezaugarri kuantitatiboen loci-ren mapak egiteko zehaztasuna. Theor. Genet aplikazioa. 84, 803-811 (1992).
- 28. Voorrips, RE Mapchart: lotura-mapen eta QTL-ak grafikoki aurkezteko softwarea. J. Hered. 93, 77-78 (2002).
- 29. Hirsch, CD et al. Spud DB: meatzaritza-sekuentziak, genotipoak eta fenotipoak patata-hazkuntza bizkortzeko baliabidea. Landareen Genoma. 7, https://doi.org/ 10.3835/plantgenome2013.12.0042 (2014).
- 30. Bankevich, A. et al. SPAdes: genomaren muntaketa algoritmo berria eta bere aplikazioak zelula bakarreko sekuentziaziorako. J. Informatika. Biol. 19, 455-477 (2012).
- 31. Sharma, SK et al. Patatentzako erreferentziazko kromosoma eskalako pseudomolekulak eraikitzea: patataren genoma mapa genetiko eta fisikoekin integratzea. G3 Geneak Genomak Genet. 3, 2031-2047 (2013).
- 32. Fernandez-Pozo, N. et al. Sol Genomics Network (SGN) - genotipotik fenotipora hazkuntzara. Azido nukleikoak. 43, D1036-D1041 (2015).
- 33. Kim, S. et al. Piper beroaren genomaren sekuentziak pikaren bilakaeraren inguruko argibideak ematen ditu Capsicum espezie. Nat. Genet. 46, 270-278 (2014).
- 34. Santillan Martinez, MI et al. Tomatearen suszeptibilitate genearen CRISPR/Cas9 PMR4 oidioaren aurkako erresistentziarako zuzendutako mutagenesia. BMC Landare Biol. 20, 1-13 (2020).
- 35. Liang, G., Zhang, H., Lou, D. & Yu, D. CRISPR/Cas9-n oinarritutako landare genomaren ediziorako sgRNA oso eraginkorrak hautatzea. Zientzia. Rep. 6, 1-8 (2016).
- 36. Stemmer, M., Thumberger, T., Del Sol Keyer, M., Wittbrodt, J. & Mateo, JL CCTop: CRISPR/Cas9 helburu iragartzeko tresna intuitibo, malgu eta fidagarria. PLoS ONE 10,1-11 (2015).
- 37. Zuker, M. Mfold web zerbitzaria azido nukleikoen tolesketa eta hibridazioa iragartzeko. Azido nukleikoak. 31, 3406-3415 (2003).
- 38. Chari, R., Yeo, NC, Chavez, A. & Church, GM SgRNA Scorer 2.0: CRISPR/Cas9 jarduera iragartzeko espezieen araberako eredua. ACS sintetizadorea. Biol. 6, 902-904 (2017).
- 39. Visser, RGF in Landare-ehunen hazkuntzarako eskuliburua 301-309 (Springer, 1991).
Lehiaketan parte hartzen interesak
Egileek ez dute lehia aldarrikatzen.
Informazio osagarria
Informazio osagarria Lineako bertsioak webgunean eskuragarri dagoen material osagarria du https://doi.org/10.1038/s41467-021-24267-6.
korrespondentzia eta material eskaerak CWBBri zuzendu behar zaizkio
Berdinen arteko informazioa berrikustea Natura Komunikazioak eskerrik asko Roger Chetelat-i eta beste iritzi-emaile anonimoari, lan honen parekideen berrikuspenean egindako ekarpenagatik. parekideen berrikuspen txostenak eskuragarri daude.
Berrargitalpenak eta baimenen informazioa da eskuragarri http://www.nature.com/reprints
Argitaratzailea's oharra Springer Nature-k berretsi egiten du argitaratutako mapa eta instituzioen afiliazioen jurisdikzio-erreklamazioei dagokienez.
Eskerrak
Veronica Tammy Soputrok bi patata genotipoen eraldaketan emandako laguntza aitortzen dugu pAGM-rekin: CRISPRASli, Gilo Pleunis, Iris Smits, Niki Vorgia, Hidde Knuiman, Maurice Geurts, Anja van Heteren eta Torsten van der BSc eta MSc ikasleen laguntza. Schriek-ek populazio mapak fenotipatzen lagundu izanagatik, eta Tess Lucas RNA laginak sortzeagatik. Gainera, Solynta eta Wageningen Unibertsitateko Unifarm negutegiko langileei eskertzen diegu landareen mantentze eta hazien erauzketan emandako laguntzagatik. Proiektu honek Herbehereetako Ikerketa Zientifikorako Erakundearen diru-laguntza jaso du (Diru-laguntzaren IDa: NWA.17.023).
Autorearen ekarpenak
E.-JEk esperimentuak diseinatu eta gauzatu zituen eta eskuizkribua idatzi zuen. AvdB-k WGS, KASP markatzailea eta bioinformatika ikuspegiak diseinatu eta exekutatu zituen. SvH, RGFV, CWBB, MEdV eta PL-k mapa genetikoa aztertzeko eta ezaugarritze funtzionalaren ikuspegia diseinatzen lagundu zuten. sli. RGFV, CWBB eta PL-ek eskuizkribua berrikusi eta iruzkindu zuten.
I (S) Q) Open Access Artikulu hau Creative Commons Aitortu 4.0 Nazioarteko Lizentziapean dago. Erabilera, partekatzea, egokitzea, banatzea eta erreproduzitzea baimentzen du edozein euskarritan edo formatuan, betiere jatorrizko egileari eta iturriei kreditu egokia ematen baduzu. esteka Creative Commons lizentziarekin, eta adierazi aldaketak egin ziren ala ez. Irudiak edo artikulu honetako beste material batzuen artikuluak Creative Commons lizentziaren barruan sartzen dira, materialaren kreditu lerroan kontrakoa adierazi ezean. Artikulua Creative Commons lizentziaren barruan sartzen ez bada eta aurreikusitako erabilera estatutu araudiak onartzen ez badu edo baimendutako erabilera gainditzen badu, copyrightaren titularraren baimena eskuratu beharko duzu. Lizentzia honen kopia bat ikusteko, bisitatu http://creativecommons.org/ lizentziak/erantzun/4.0/.









